6.5 Estructura de RNA pequeños con función reguladora
Esta es la estructura del RNA nuclear pequeño U1 (con 163 nt).
algunas de las proteínas que se asocian con él para formar la ribonucleoproteína U1 (un componente del ayustosoma, pág. 300).
Esta es la estructura de una parte de un microRNA (pág. 68) llamado let-7, que se empareja con su RNA mensajero diana, llamado lin-41.
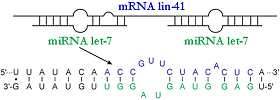
la región complementaria del mRNA.
las bases desemparejadas.
Esta es la estructura de un ribointerruptor (pág. 68).
Estilo:
(un análogo de la guanina).
por el ribointerruptor

Animación del cambio conformacional:
Para que el ligando pueda unirse, la base de uno de los residuos nucleótidos debe apartarse de su posición interior: .
Referencias:
- Estructura central de la ribonucleoproteína snRNP U1 humana (3PGW.pdb) doi:10.2210/pdb3pgw/pdb
- Estructura de un modelo que emula el complejo entre miRNA let-7 y mRNA lin-41, del gusano Caenorhabditis elegans (2KPV.pdb) doi:10.2210/pdb2kpv/pdb
- Figura adaptada de M. Cevec et al. (2010) doi: 10.1093/nar/gkq640 (acceso abierto).
- Estructura de un ribointerruptor PreQ1 de clase I en los estados con y sin ligando unido. (3Q50.pdb, 3Q51.pdb) doi:10.2210/pdb3q50/pdb y 10.2210/pdb3q51/pdb
- The morph server: a standardized system for analyzing and visualizing macromolecular motions in a database framework. WG Krebs, M Gerstein (2000) Nucleic Acids Res. 28: 1665-75. The Yale Morph Server, http://www.molmovdb.org/